Kim-Hellmuth Lab
Funktionelle Immungenomik


Forschungsgebiet
- Genetischer Einfluss auf die menschliche Immunantwort
- Genetik des Immunsystems in verschiedenen Populationen
- Humane perinatale Immunzellentwicklung
- Molekulare Charakterisierung der COVID-19 Erkrankung bei Kindern und jungen Erwachsenen
Prof. Dr. med. Sarah Kim-Hellmuth
✉ Sarah.Kimhellmuth@med.uni-muenchen.de
🐦/X: @skimhellmuth
Die Junge Akademie Profil: hier
#InnovativeFrauen Profil: hier

Das menschliche Immunsystem spielt eine Schlüsselrolle in der Abwehr eindringender Keime, aber auch bei Autoimmun-, Krebs- und Stoffwechselerkrankungen sowie in Alterungsprozessen. Genomweite Assoziationsstudien dieser Erkrankungen haben Hunderte von genetischen Loci in Genen des Immunsystems identifiziert und deuten somit auch auf eine zentrale mechanistische Beteiligung des Immunsystems hin. Für die überwiegende Mehrheit dieser genetischen Varianten ist jedoch der Wirkmechanismus und ihre Kontextabhängigkeit bislang nicht erforscht. Die Untersuchung des genetischen Einflusses auf die Immunantwort wird ferner durch die Komplexität des Immunsystems erschwert, welches aus vielen verschiedenen Zelltypen besteht, die auf eine Vielzahl von Signalen reagieren, miteinander interagieren und zu unterschiedlichen Zeitpunkten ihre Effektorfunktionen ausüben.
Das übergeordnete Ziel unserer Forschungsgruppe ist die Charakterisierung des genetischen Einflusses auf die menschliche Immunantwort, um unser Verständnis von krankheitsassoziierten Varianten zu verbessern und Fragen der Plastizität der Genomfunktion zu beantworten. Hierfür integrieren wir modernste genomische und funktionelle genetische Ansätze, um regulatorische genetische Varianten, die mit molekularen Prozessen der Immunantwort assoziiert sind, sogenannten molecular quantitative trait loci (molQTLs), zu charakterisieren. Basierend auf diesen molQTLs werden Vorhersagemodelle entwickelt, die es ermöglichen sollen, Patienten in Zukunft anhand ihres genetischen Immunprofils stratifizieren zu können.

Die Zusammensetzung und Reifung menschlicher Immunzellen zeigen sowohl bei Früh- und Termingeborenen eine sehr hohe interindividuelle Variabilität. Quantitative und qualitative Veränderungen der neonatalen Neutrophilen können vermutlich zu einer erhöhten Anfälligkeit für bakterielle Infektionen und neonatale Sepsis beitragen. Diese sind noch immer auptursachen für Kindersterblichkeit und chronische Erkrankungen. Diese Variabilität wird durch genetisch festgelegte Programme, die ständig wechselnde Umwelt und die Interaktion zwischen diesen beiden Faktoren (GxE-Interaktion) bestimmt. Komplexe perinatale Modelle in Mäusen und anderen Modellsystemen ermöglichen eine umfassende Erforschung der Umweltfaktoren, die die perinatale Immunzellentwicklung beeinflussen. Dennoch sind die genetischen Grundlagen der perinatalen Immunzellvariabilität beim Menschen bis heute kaum bekannt und weitestgehend unerforscht.
In diesem Projekt wird die Rolle von cis-regulatorischen Varianten auf die Proteinexpression während der perinatalen Immunzellentwicklung bei menschlichen Neugeborenen untersucht. Dazu verwenden wir die Munich Preterm and Term clinical (MUNICH-PreTCl) Geburtskohorte. Durch die Integration von Proteomprofilen und Genotypdaten der Teilnehmer werden wir genetische Varianten identifizieren, die die Variabilität der Proteinhäufigkeit in neonatalen Blutproben zu definierten Schwangerschaftszeitpunkten bestimmen. Diese so genannten Protein Quantitative Trait Loci (pQTL) geben Aufschluss darüber, wie die Genetik individuelle Phänotypen definiert, indem wir die anschließende Modulation verschiedener Proteinexpressionsprofile betrachten.
COVID-19 ist eine Viruserkrankung, die durch das SARS-CoV-2 Virus (severe acute respiratory syndrome coronavirus 2) verursacht wird und durch einen höchst variablen Krankheitsverlauf gekennzeichnet ist. Die Mehrheit aller Patienten zeigt einen milden Verlauf mit Fieber und Husten. Ein kleinerer Teil der Patienten erleidet jedoch schwerwiegende Krankheitsverläufe und muss stationär oder sogar intensivmedizinisch behandelt werden. Während die Infektion bei Kindern einen milderen Verlauf als bei Erwachsenen aufzuweisen scheint, so sind dennoch alle Altersgruppen betroffen und auch schwere Verläufe mit Todesfällen sind seit Ausbruch der Pandemie beschrieben. Warum Kinder einen anderen Verlauf als Erwachsene und sogar in verschiedenen Altersklassen unterschiedliche Verläufe aufweisen, ist derzeit unbekannt.
Wir haben daher eine COVID-19-Studie initiiert, um die genetischen und Umweltrisikofaktoren von COVID-19 bei pädiatrischen und erwachsenen Patienten zu untersuchen. Unsere Forschungsgruppe integriert hierfür Daten des Immunprofils mit Multi-Omics auf zahlreichen molekularen Ebenen (Genom, Transkriptom, Proteom, Metabolom), um die Immunantwort auf SARS-CoV-2 detailliert zu charakterisieren und besser zu verstehen. Folgende Fragen werden hierbei beantwortet:
- Warum verläuft COVID-19 bei Kindern anders als bei Erwachsenen?
- Welche genetischen und immunologischen Risikofaktoren tragen zu diesen Unterschieden bei?
- Können wir diese Faktoren nutzen, um schwere Verläufe vorherzusagen?
Unsere prospektive Studie wird im Rahmen der Child Health Alliance Munich (CHANCE) am Dr. von Haunerschen Kinderspital der Ludwig-Maximilians-Universität (LMU) München und der Klinik für Kinder- und Jugendmedizin der Technischen Universität München (TUM) und München Klinik Schwabing durchgeführt. Die Studie ist auch aktiv an nationalen (Deutsche COVID-19 OMICS-Initiative) und internationalen (COVID-19 Host Genetics Initiative) COVID-19-Initiativen beteiligt, um gemeinsam gegen diese Pandemie vorzugehen.
































Ausgewählte Publikationen:
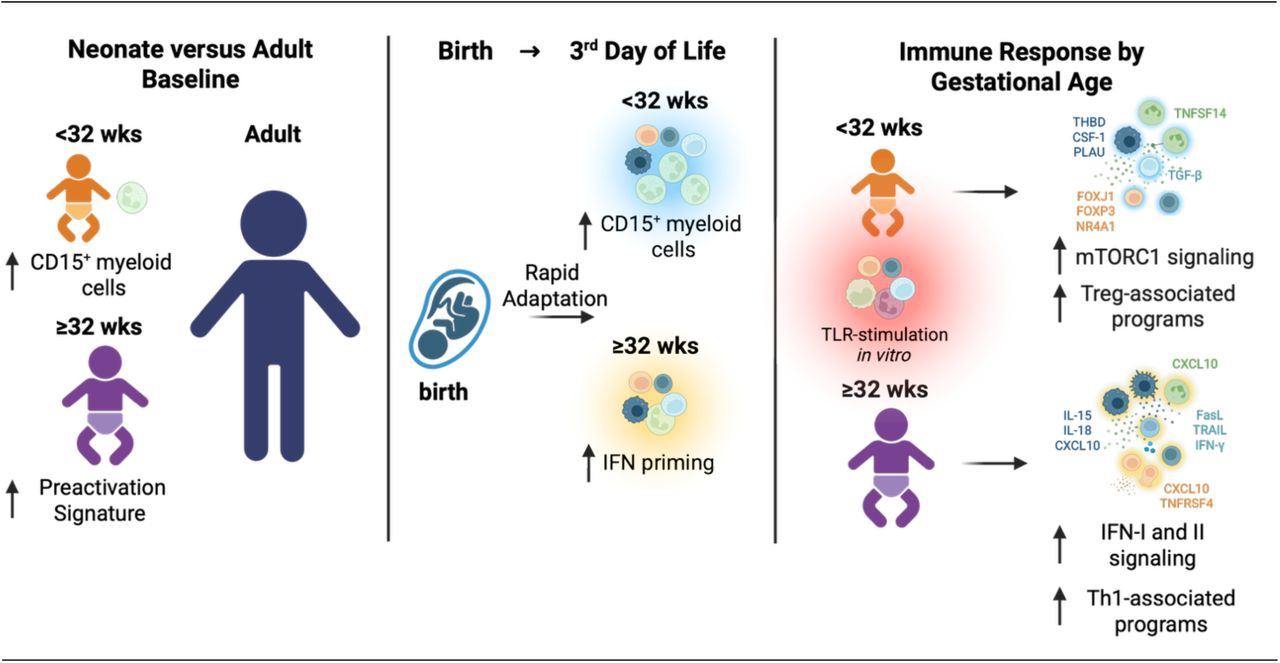
1. Rothämel, P., Mattia, A., Corey, M. I., Puzek, B., Wiesel, J., Michael-Kuschel, P., Klein, C., Sperandio, M., Henneke, P., Nussbaum, C., & Kim-Hellmuth, S. (2026). Human neonatal CITE-seq atlas identifies an immune transition at 32 weeks’ gestation from CD15⁺ myeloid-dominated to interferon-primed immunity. bioRxiv, 2026.04.01.715643.
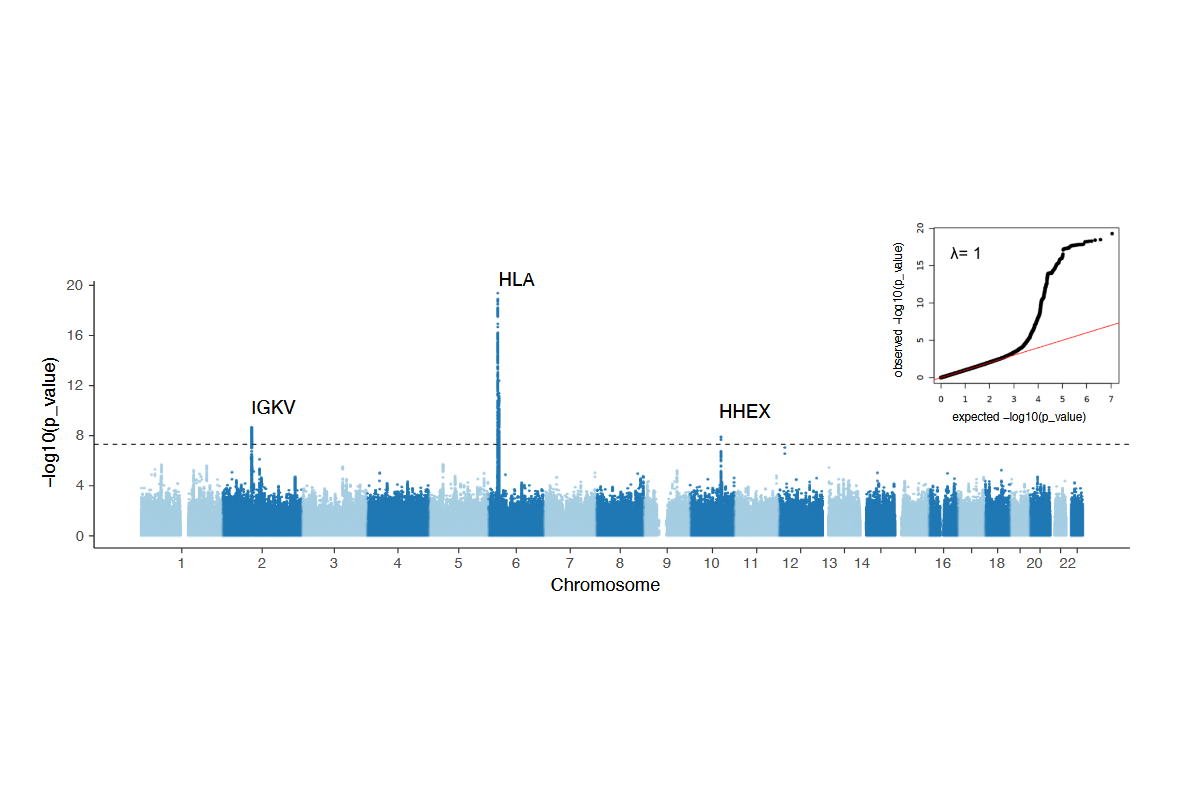
2. Puzek, B., Wratil, P. R., Janke, C., Le Thi, T. G., Rubio-Acero, R., Lupoli, G., Schoof, I. C., Stern, M., Zhelyazkova, A., Rech, J., Choukér, A., Koletzko, B., Wieser, A., Török, H. P., Castelletti, N., Keppler, O. T., Geldmacher, C., Hornung, V., Zeggini, E., Adorjan, K., Hoelscher, M., Koletzko, S., & Kim-Hellmuth, S. (2025). Genetic variation in HLA, IGKV and HHEX loci influence mRNA vaccine-induced long-lasting humoral protection against COVID-19. medRxiv, 2025.10.21.25337971.
3. Franz, T. M., Punathil, R. K., Soto-Beasley, A. I., Strongosky, A., Walton, R. L., Kim-Hellmuth, S., Springer, W., Dulski, J., Ross, O. A., Jaramillo-Koupermann, G., Alarcon, F., & Wszolek, Z. K. (2025). Screening for PRKN and PINK1 mutations in Ecuadorian patients with early-onset Parkinson's Disease. Neurologia i neurochirurgia polska, 59(1), 56–61.
4. Santos-Peral, A., Zaucha, M., Nikolova, E., Yaman, E., Puzek, B., Winheim, E., Goresch, S., Scheck, M. K., Lehmann, L., Dahlstroem, F., Karimzadeh, H., Thorn-Seshold, J., Jia, S., Luppa, F., Pritsch, M., Butt, J., Metz-Zumaran, C., Barba-Spaeth, G., Endres, S., Kim-Hellmuth, S., Waterboer, T., Krug, A. B., & Rothenfusser, S. Basal T cell activation predicts yellow fever vaccine response independently of cytomegalovirus infection and sex-related immune variations. Cell Rep Med, 6(2), 101946 (2025).
5. Schmidt, A., Casadei, N., Brand, F., Demidov, G., Vojgani, E., Abolhassani, A., Aldisi, R., Butler-Laporte, G., DeCOI host genetics group, Alawathurage, T. M., Augustin, M., Bals, R., Bellinghausen, C., Berger, M. M., Bitzer, M., Bode, C., Boos, J., Brenner, T., Cornely, O. A., Eggermann, T., Erber, J., Feldt ,T., Fuchsberger, C., Gagneur, J., Göpel, S., Haack, T., Häberle, H., Hanses, F., Heggemann, J., Hehr, U., Hellmuth, J. C., Herr, C., Hinney, A., Hoffmann, P., Illig, T., Jensen, B. O., Keitel, V., Kim-Hellmuth, S., [...], Motameny, S., Nothnagel, M., Riess, O., Schulte, E. C., & Ludwig, K. U. Systematic assessment of COVID-19 host genetics using whole genome sequencing data. PLoS Pathog 20(12) (2024).
6. Nussbaum, C. & Kim-Hellmuth, S. Unlocking the genetic influence on milk variation and its potential implication for infant health. Cell Genom. 4, 100676 (2024).
7. Kasela, S., Aguet, F., Kim-Hellmuth, S., Brown, B. C., Nachun, D. C., Tracy, R. P., Durda, P., Liu, Y., Taylor, K. D., Johnson, W. C., Berg, D. V. D., Gabriel, S., Gupta, N., Smith, J. D., Blackwell, T. W., Rotter, J. I., Ardlie, K. G., Manichaikul, A., Rich, S. E., Barr, R. G. & Lappalainen, T. Interaction molecular QTL mapping discovers cellular and environmental modifiers of genetic regulatory effects. Am J Hum Genet 111(1) (2024).
8. Kerimov, N., Tambets, R., Hayhurst, J. D., Rahu, I., Kolberg, P., Raudvere, U., Kuzmin, I., Chowdhary, A., Vija, A., Teras, H. J., Kanai, M., Ulirsch, J., Ryten, M., Hardy, J., Guelfi, S., Trabzuni, D., Kim-Hellmuth, S., Rayner, W., Finucane, H., Peterson, H., Mosaku, A., Parkinson, H. & Alasoo, K. eQTL Catalogue 2023: New datasets, X chromosome QTLs, and improved detection and visualisation of transcript-level QTLs. PLoS Genet. 19, e1010932 (2023).
9. Flynn, E., Tsu, A., Kasela, S., Kim-Hellmuth, S., Aguet, F., Ardlie, K. G., Bussemaker, H. J., Mohammadi, P. & Lappalainen, T. Transcription factor regulation of eQTL activity across individuals and tissues. Plos Genet 18 (2022).
10. Brandt, M. K., Kim-Hellmuth, S., Ziosi, M., Gokden, A., Wolman, A., Lam, N., Recinos, Y., Hornung, V. K., Schumacher, J. & Lappalainen, T. An autoimmune disease risk variant: A trans master regulatory effect mediated by IRF1 under immune stimulation? PLoS Genet, 17(7), (2021).
11. Warnat-Herresthal, S., Schultze, H., Shastry, K. L., Manamohan, S., Mukherjee, S., Garg, V., Sarveswara, R., Händler, K., Pickkers, P., Aziz, N. A., Ktena, S., Tran, F., Bitzer, M., Ossowski, S., Casadei, N., Herr, C., Petersheim, D., Behrends, U., Kern, F., Fehlmann, T., Schommers, P., Lehmann, C., Augustin, M., Rybniker, J., Altmüller, J., Mishra, N., Bernardes, J. P., Krämer, B., Bonaguro, L., Schulte-Schrepping, J., Domenico, E. D., Siever, C., Kraut, M., Desai, M., Monnet, B., Saridaki, M., Siegel, C. M., Drews, A., Nuesch-Germano, M., Theis, H., Heyckendorf, J., Schreiber, S., Kim-Hellmuth, S., […], Deutsche COVID-19 Omics Initiative (DeCOI), Giamarellos-Bourboulis, E. J., Kox, M., Becker, M., Cheran, S., Woodacre, M. S., Goh, E. L. & Schultze, J. L. Swarm Learning for decentralized and confidential clinical machine learning. Nature 1–7 (2021).
12. de Goede, O. M., Nachun, D. C., Ferraro, N. M., Gloudemans, M. J., Rao, A. S., Smail, C., Eulalio, T. Y., Aguet, F., Ng, B., Xu, J., Barbeira, A. N., Castel, S. E., Kim-Hellmuth, S., Park, Y., Scott, A. J., Strober, B. J., GTEx Consortium, Brown, C. D., Wen, X., Hall, I. M., Battle, A., Lappalainen, T., Im, H. K., Ardlie, K. G., Mostafavi, S., Quertermous, T., Kirkegaard, K. & Montgomery, S. B. Population-scale tissue transcriptomics maps long non-coding RNAs to complex disease. Cell (2021).
13. GTEx Consortium#. The GTEx Consortium atlas of genetic regulatory effects across human tissues. Science 369, 1318-1330 (2020). #Lead analyst: Kim-Hellmuth, S.
>> Science cover and Introduction to Special Issue
>> Press releases: here and here
14. Kim-Hellmuth, S.†*, Aguet, F.*, Oliva, M., Muñoz-Aguirre, M., Kasela, S., Wucher, V., Castel, S. E., Hamel, A. R., Viñuela, A., Roberts, A. L., Mangul, S., Wen, X., Wang, G., Barbeira, A. N., Garrido-Martin, D., Nadel, B., Zou, Y., Bonazzola, R., Quan, J., Brown, A., Martinez-Perez, A., Soria, J. M., GTEx Consortium, Getz, G., Dermitzakis, E., Small, K. S., Stephens, M., Xi, H. S., Im, H. K., Guigó, R., Segre, A. V., Stranger, B. E., Ardlie, K. G. & Lappalainen, T. Cell type specific genetic regulation of gene expression across human tissues. Science 369 (2020).
>> Featured in 'This week in Science'
>> Press releases: here and here
15. Oliva, M.*, Muñoz-Aguirre, M.*, Kim-Hellmuth, S.*, Wucher, V., Gewirtz, A., Cotter, D., Parsana, P., Kasela, S., Balliu, B., Viñuela, A., Castel, S. E., Mohammadi, P., Aguet, F., Zou, Y., Khramtsova, E., Skol, A., Garrido-Martin, D., Reverter, F., Brown, A., Evans, P., Gamazon, E., Payne, A., Bonazzola, R., Barbeira, A. N., Hamel, A. R., Martinez-Perez, A., Soria, J. M., GTEx Consortium, Pierce, B., Stephens, M., Eskin, E., Dermitzakis, E., Segre, A. V., Im, H. K., Engelhardt, B., Ardlie, K. G., Montegomery, S., Battle, A., Lappalainen, T., Guigó, R. & Stranger, B. E. The impact of sex on gene expression and its genetic regulation across human tissues. Science 369 (2020).
>> Science Perspective and selected media coverage: Deutschlandfunk Forschung aktuell
>> Press releases: here and here
16. Demanelis, K., Jasmine, F., Chen, L. S., Chernoff, M., Tong, L., Delgado, D., Zhang, C., Shinkle, J., Sabarinathan, M., Lin, H., Ramirez, E., Oliva, M., Kim-Hellmuth, S., Stranger, B. E., Lai, T.-P., Aviv, A., Ardlie, K. G., Aguet, F., Ahsan, H., GTEx Consortium, Doherty, J. A., Kibriya, M. G. & Pierce, B. L. Determinants of telomere length across human tissues. Science 369 (2020).
17. Kim-Hellmuth, S.†, Bechheim, M., Pütz, B., Mohammadi, P., Nédélec, Y., Giangreco, N., Becker, J., Kaiser, V., Fricker, N., Beier, E., Boor, P., Castel, S. E., Nöthen, M. M., Barreiro, L. B., Pickrell, J. K., Müller-Myhsok, B., Lappalainen, T., Schumacher, J. & Hornung, V. Genetic regulatory effects modified by immune activation contribute to autoimmune disease associations. Nat Commun 8, 266 (2017).
18. Kim-Hellmuth, S. & Lappalainen, T. Concerted Genetic Function in Blood Traits. Cell 167, 1167–1169 (2016).
19. Hornung, V., Ellegast, J., Kim, S., Brzózka, K., Jung, A., Kato, H., Poeck, H., Akira, S., Conzelmann, K.-K., Schlee, M., Endres, S. & Hartmann, G. 5'-Triphosphate RNA is the ligand for RIG-I. Science 314, 994–997 (2006).
†Corresponding author, *Equally contributing author
04/2026

Neues Labormitglied: Masterstudentin Tanja Pock
03/2026

Neues Labormitglied: Postdoc Shi-Fang Li

Paula Rothämel erhält den Best Poster-Preis bei der GfH-Jahrestagung
02/2026

Neues Labormitglied: Clinician Scientist Franziska Füchsl
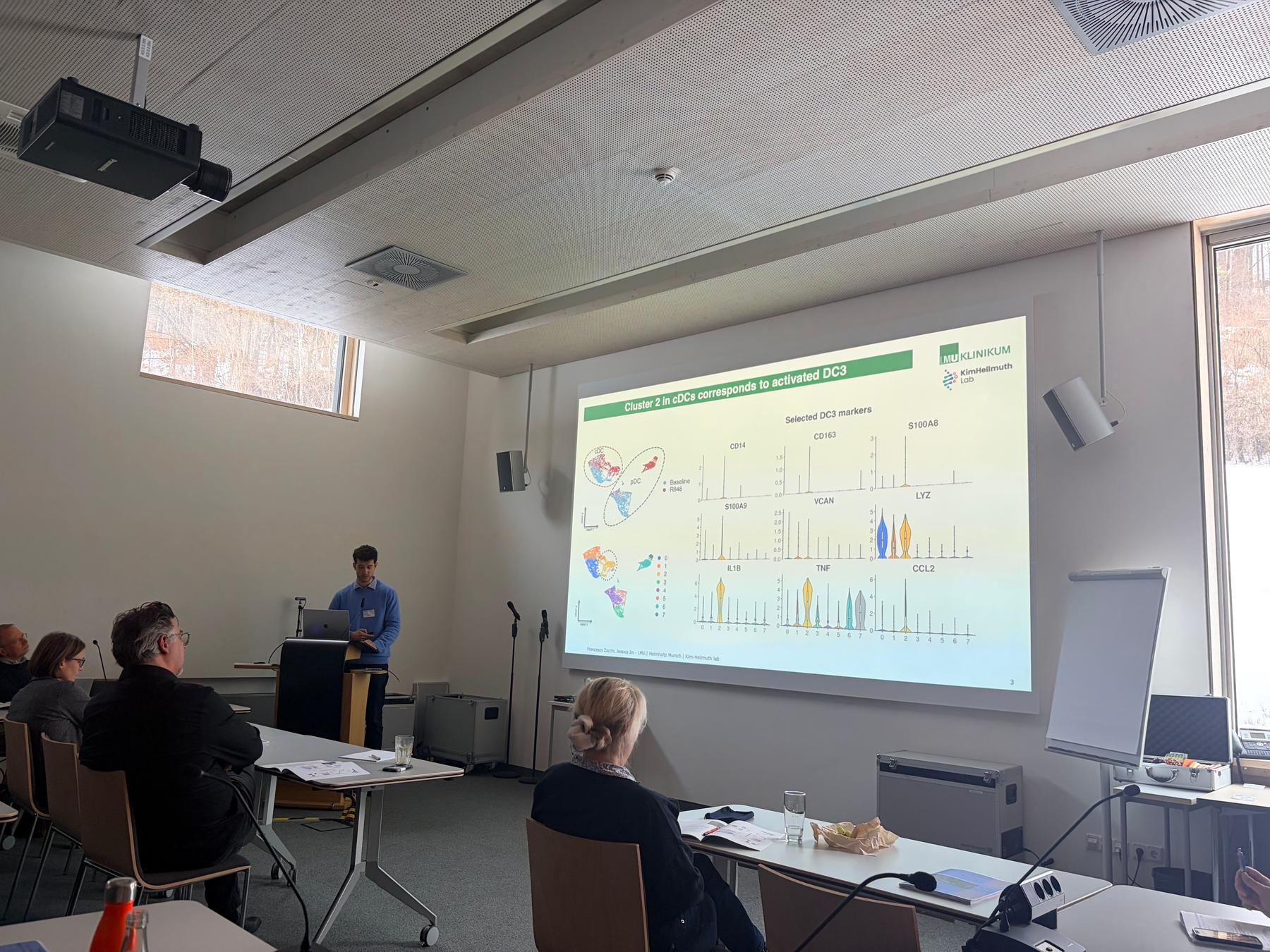
Francesco Zocchi hält einen Vortrag beim DGfI AKDC-Treffen

Irene Namara hält einen Vortrag beim DGfI AKDC-Treffen
11/2025

Paula Rothämel beim CoPILOT Retreat

Pauline Kuschel beim CoPILOT Retreat

Maria Corey beim CoPILOT Retreat
10/2025
09/2025

Neues Labormitglied:
Dr. cand. med. Francesco Zocchi

Neues Labormitglied:
Medizinstudentin Eva Herold
08/2025

Neues Labormitglied:
Medizinstudentin Maria Corey
07/2025
Sathya Darmalinggam verteidigt ihre PhD-Dissertation
06/2025

04/2025

Neues Labormitglied:
Medizinstudentin Fintan Viebahn
03/2025

Neues Labormitglied:
PhD Studentin Irene Namara


01-02/2025


Sarah Kim-Hellmuth wird in der STEMPASSION Women in Science Ausstellung vertreten

Jessica Jin hält einen Vortrag beim DGfI AKDC-Treffen
09/2024

Neues Labormitglied:
Senior Bioinformatician Susanne Horn, PhD

Neues Labormitglied:
Medizinstudentin Chiara Geiger

Neues Labormitglied:
PhD Student Furkan Büyükgöl
07/2024

Neues Labormitglied:
Clinician Scientist Dr. med. Paula Rothämel
06/2024

04/2024

Neues Labormitglied:
Wissenschaftliche Mitarbeiterin Juliane Klein

Neues Labormitglied:
Clinician Scientist Dr. med. Jessica Jin
03/2024

Offizieller Beginn unseres ImmGenDC-Uganda Teams in Kyamulibwa

Neues Labormitglied:
Masterstudentin Franziska Schweiger

Neues Labormitglied:
Masterstudentin Deniz Eser

Neues Labormitglied:
Medizinstudentin Sophia Grotz
02/2024

01/2024

Start unseres ERC Starting Grant Projektes ImmGenDC in Uganda

Neues Labormitglied:
Postdoc Marie Bourdon, PhD

Neues Labormitglied:
Dr. cand. med. Aleksandra Jucha
12/2023

Neues Labormitglied:
Medizinstudentin Mara Franzl
11/2023

10/2023

Podiumsdiskussion beim Retreat des LMU Medical & Clinician Scientist Programmes (MCSP)

Neues Labormitglied:
PhD Student Alessandro Mattia
09/2023

Sathya Darmalinggam's Posterpräsentation auf der ersten Joint-Konferenz der Société Française d’Immunologie und der Deutschen Gesellschaft für Immunologie

Tuguldur Tumurbaatar's Posterpräsentation auf der ersten Joint-Konferenz der Société Française d’Immunologie und der Deutschen Gesellschaft für Immunologie
06/2023

Neues Labormitglied:
Medizinstudentin Laura Jänisch
05/2023

Das Kinderbuch “Young Scientists” der Jungen Akademie erscheint mit Sarah Kim-Hellmuth als eine von 30 Forschenden
04/2023


Neues Labormitglied:
Dr. cand. med. Mirjam Schobel

Neues Labormitglied:
Masterstudentin Pauline Kuschel
03/2023

Neues Labormitglied:
Bioinformatician Nicolás Lichilín, PhD

Neues Labormitglied:
Medizinstudentin Lea Steinberg
02/2023


Neues Labormitglied:
Research Fellow Dr. med. Tobias Franz
01/2023

Neues Labormitglied:
Masterstudentin Preeti Thiyagarajan

Neues Labormitglied:
Medizinstudentin Ekin Yaman
11/2022


Neues Labormitglied:
Masterstudent Tuguldur Tumurbaatar

Neues Labormitglied:
Dr. cand. med. Jana Wiesel
09-10/2022


07-08/2022


Neues Labormitglied:
Masterstudent Nishant Chintalagiri
05-06/2022

Podiumsdiskussion mit Sarah Kim-Hellmuth beim Festakt zum 175. Geburtstages des Hauner

03-04/2022


Neues Labormitglied:
Dr. cand. med. Theresa Haslbeck
11/2021

Neues Labormitglied:
PhD Studentin Barbara Puzek

10/2021


09/2021

Neues Labormitglied:
PhD Studentin Luise Zeckey
05-06/2021


Carola Kaltenhauser's Posterpräsentation auf der 15. Kongress für Infektionskrankheiten und Tropenmedizin
04/2021


Offizieller Start der Helmholtz-Nachwuchsgruppe "Immunogenomics"
03/2021

11-12/2020

Unsere COVID-19 Fallbeschreibung in einem Patienten mit Down-Syndrom im Wissenschaftsmagazin JPIDS

Neues Labormitglied:
Dr. cand. med. Alina Czwienzek
10/2020

Neues Labormitglied:
PhD Studentin Sathya Darmalinggam

Neues Labormitglied:
Modul 6 Student Jöran Sarazzin
09/2020



Neues Labormitglied:
Dr. cand. med. Ben Wendel


08/2020

Neues Labormitglied:
Modul 6 Studentin Anda Ardeoan
06/2020

04/2020

Neues Labormitglied:
Dr. cand. med. Carola Kaltenhauser


03/2020

Gründung der Päd-COVID-19 Studie


Laborausflug Sommer 2025

Herzlichen Glückwunsch zu deinem PhD, Sathya!

Unsere Gruppe bei Helmholtz Girls' Day 2025

Posterpräsentation beim DGfI AKDC-Treffen

Posterpräsentation beim CoPILOT Retreat

ImmGenDC Uganda Team-Meeting

Teilnahme am CSAMA Summer School in Brixen

Marie und Jessica am Wellcome Genome Campus

Cake-Day nach ESHG 2024

Unsere Gruppe beim ESHG 2024

Besuch auf der Oide Wiesn

Teilnahme an SFI-DGfI 2023 in Strasbourg

ITG Retreat 2023 am Starnberger See

Laborausflug Sommer 2023

Willkommen in der Gruppe, Jana und Tuulu!

CompHealth Retreat 2021 am Helmholtz München

Sathya und Barbara beim CGSI 2022

Vielen Dank für Euren Einsatz beim Benefizkonzert für Kinder in der Ukraine!

Laborausflug Sommer 2022

Willkommen in der Gruppe, Theresa!

Gruppenfoto nach unserem ersten Päd-COVID-19 Symposium

Willkommen in der Gruppe, Luise!

Erster Biergartenbesuch nach einem langen Lockdown

Open positions:
We are actively looking to expand our group at all levels (postdocs, senior and junior staff scientists, graduate students, interns). Given our interdisciplinary work we offer both dry and wet lab projects and are looking for highly motivated individuals with diverse scientific backgrounds (immunologists, clinicians, computational biologists, statistical geneticists, data scientists).
- Fascinated by the immune system and its complexity and diversity among us human beings?
- Driven to better understand genetic gene regulation and its role in immune-related diseases?
- Interested in applying cutting-edge genomics technologies and analytical approaches to answer some of the pressing questions in genetics & genomics and immunology?
- Enjoy working in an interdisciplinary and collaborative team surrounded by a vibrant scientific environment?
Then look no more!
Our group is dedicated to better understand the genetic basis of human immune response variation and translate those insights into the clinic to improve every day medical decision-making. Located both at Helmholtz Munich and the LMU University hospital we are embedded and collaborate in a wide scientific network, in particular with the Computational Health Center, the Department of Pediatrics, the Biomedical Center, the Gene Center Munich and of course nationally and internationally.
If you are interested in discussing projects or job opportunities please get in touch via email. This can be even very early before your potential start or before major conferences to meet informally.
Diversity and inclusivity are key values in our group. We welcome applicants from all backgrounds especially from underrepresented and underprivileged backgrounds.
Kim-Hellmuth Lab
Kinderklinik und Kinderpoliklinik im Dr. von Haunerschen Kinderspital Klinikum der Universität München, LMU München









